Strumenti per elettroforesi capillare (CE)
I sistemi Spectrum e Spectrum Compact CE forniscono soluzioni scalabili per l'analisi dei frammenti di DNA per i laboratori forensi e per l'analisi di linee cellulari e campioni misti per i laboratori di ricerca. Spectrum Compact è stato progettato anche per l'analisi del sequenziamento Sanger, supportando la conferma NGS e CRISPR-cas9.
Strumenti per elettroforesi capillare
Confronto tra i sistemi Spectrum CE
| Spettro CE | Spectrum Compact CE | |
|---|---|---|
| Panoramica | Sistema CE ad alta capacità produttiva ideale per laboratori di medie e grandi dimensioni che trattano molti campioni | Sistema CE da banco ideale per i laboratori più piccoli che desiderano aumentare l'efficienza |
| Applicazioni | Analisi dei frammenti | Sequenziamento Sanger, analisi dei frammenti |
| Numero di capillari | 8 (24 in arrivo) | 4 |
| Lunghezza dell'array di capillari | 36 cm | 36 cm |
| Numero massimo di colori del colorante | 8 | 6 |
| Produzione | Alta produttività Quattro piastre da 96 pozzetti con accesso continuo |
Produttività medio-bassa Quattro provette a striscia da 8 pozzetti |
| Piattaforma informatica | Computer e monitor separati | Touch screen integrato con computer incorporato |
| Polimero | Polimero4 | Polimero4 e polimero7 |
| Tracciabilità dei materiali di consumo | RFID | Codice a barre 2D |
| Tipo di file di dati | .fsa e .promega | .fsa e .ab1 |
| Analisi secondaria | GeneMarkerHID® Spectrum | Software di sequenziamento GeneMarkerHID® Spectrum ProView |
| Peso | 103 kg (228 libbre) | 45 kg (99 libbre) |
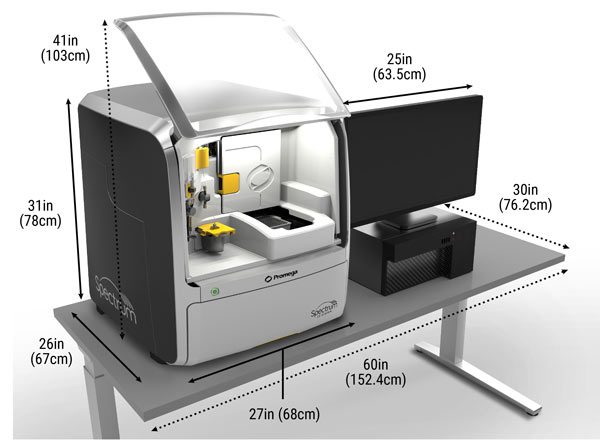
| Dimensioni | 68 cm L x 68 cm P x 77 cm A | 40 cm L x 60 cm P x 60 cm A |
|

|
Introduzione all'elettroforesi capillare
L'elettroforesi capillare è un metodo per separare e identificare frammenti di DNA marcati in modo fluorescente facendoli passare attraverso capillari molto sottili riempiti di polimeri. L'uso di capillari al posto di un gel convenzionale permette di applicare un campo elettrico molto più forte, con conseguente separazione più rapida e maggiore produttività. Il processo è caratterizzato da una risoluzione a singola base e richiede piccole quantità di campione.
I campioni di DNA marcati in modo fluorescente vengono preparati per l'elettroforesi e caricati nello strumento CE. La matrice capillare viene riempita di polimero e posizionata nei pozzetti del campione. Quando la matrice capillare entra nei pozzetti, si forma una corrente elettrica e i frammenti di DNA vengono spostati elettrocineticamente nei capillari. Successivamente, le estremità della matrice capillare vengono inserite nel tampone catodico e anodico. Lo strumento applica una tensione e una temperatura specifiche per controllare la migrazione del campione attraverso la matrice capillare. I frammenti vengono separati in base alle dimensioni, con i frammenti più piccoli che si muovono più velocemente.
La fase finale è la rilevazione del campione. Quando i frammenti marcati in modo fluorescente passano davanti alla finestra di rilevamento, un laser eccita i coloranti fluorescenti. La luce emessa viene separata spettralmente e registrata da una telecamera CCD. La telecamera CCD registra la firma fluorescente di ciascun frammento e il tempo trascorso dal frammento per migrare attraverso il polimero. I dati grezzi vengono inviati al software di raccolta sotto forma di picco e sono pronti per l'analisi.
Le applicazioni comprendono l'analisi STR e il sequenziamento Sanger, oltre a molte altre funzioni quotidiane dei laboratori di ricerca forensi, accademici e clinici.

What is Sanger Sequencing?
Sanger sequencing, also known as the chain termination method, is a DNA sequencing technique that relies on selective incorporation of chain-terminating dideoxynucleotides during DNA replication, enabling precise determination of nucleotide sequences. Though newer high-throughput methods have emerged, Sanger sequencing remains a gold standard for small-scale sequencing applications due to its accuracy and reliability. It is widely used for applications such as gene validation, mutation detection, microbial identification, and confirming next-generation sequencing (NGS) results.

What is Fragment Analysis?
Fragment analysis is a molecular biology technique used to separate and analyze DNA fragments based on their size. Utilizing fluorescent labeling and capillary electrophoresis, this method allows for the precise sizing of DNA fragments differing by as little as a single nucleotide. Fragment analysis is essential in applications such as forensic casework, database sample analysis, microsatellite characterization, genotyping, mutation detection, and DNA fingerprinting.